23andme-Meu Haplogrupo mtDNA L2a1c1
Esta é uma versão para impressão do seu relatório e pode conter informações confidenciais e personalizadas.
Por favorquando terminar de imprimir.

ANTÔNIO FLORENTINO
Haplogrupo materno
Você descende de uma longa linhagem de mulheres que pode ser rastreada até o leste da África há mais de 150.000 anos. Estas são as mulheres de sua linha materna, e seu haplogrupo materno lança luz sobre a história delas.
ANTONIO, seu haplogrupo materno é L2a1c1.
À medida que nossos ancestrais se aventuravam no leste da África, eles se ramificaram em diversos grupos que cruzaram e recruzaram o globo ao longo de dezenas de milhares de anos. Algumas de suas migrações podem ser rastreadas através de haplogrupos, famílias de linhagens que descendem de um ancestral comum. Seu haplogrupo materno pode revelar o caminho percorrido pelas mulheres de sua linha materna.
Migrações de sua linha materna

Haplogrupo L
Se cada pessoa que vive hoje pudesse traçar sua linha materna ao longo de milhares de gerações, todas as nossas linhas se encontrariam em uma única mulher que viveu no leste da África entre 150.000 e 200.000 anos atrás. Embora ela fosse uma das milhares de mulheres vivas na época, apenas os diversos ramos de seu haplogrupo sobreviveram até hoje. A história de sua linha materna começa com ela.
Haplogrupo L2
Seu ramo de L é o haplogrupo L2, que surgiu de uma mulher que viveu na África há quase 90.000 anos. Mais recentemente - na verdade, apenas 4.000 anos atrás - seus descendentes fizeram parte das principais migrações bantu que os levaram da África central para o leste e o sul e fizeram de L2 o haplogrupo mais comum entre os africanos.
Origem e Migrações do Haplogrupo L2a1
Sua linha materna deriva de um ramo do haplogrupo L2 chamado L2a1. L2a1 é um ramo difundido que surgiu aproximadamente 24.000 anos atrás. No auge da Última Idade do Gelo, 20.000 anos atrás, o deserto do Saara tornou-se totalmente inabitável e começou a se expandir para o sul. As pessoas na África central com L2a1 começaram a viajar em duas direções: leste em direção ao clima mais frio das terras altas do leste e oeste em direção à costa atlântica.
Então, começando cerca de 4.000 anos atrás, dois sub-ramos de L2a1 - L2a1a e L2a1b - foram varridos com o povo de língua bantu da África Ocidental. Esses povos, que praticavam a agricultura há mil anos ou mais, começaram a expandir seu território e gradualmente introduziram sua língua e seu modo de vida aos vizinhos do leste e do sul. Hoje, tanto a L2a1a quanto a L2a1b estão bem representadas no Sudeste da África.
L2a1 também é bastante comum entre os descendentes de africanos na América do Norte e do Sul. Sua alta frequência deve-se provavelmente à concentração de L2a1 na África Ocidental, que era a principal região de abastecimento do tráfico atlântico de escravos.
L2a1c1
Seu haplogrupo materno, L2a1c1, remonta a uma mulher que viveu aproximadamente 7.000 anos atrás.
L2a1c1 é relativamente incomum entre os clientes da 23andMe.
A Expansão Bantu transformou a paisagem cultural e genética da África.
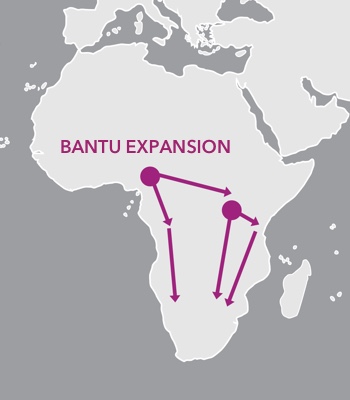
Cerca de 5.000 anos atrás, muitas pessoas na África Subsaariana ainda dependiam da caça, coleta e coleta de alimentos como principal meio de coleta de alimentos. Mas isso logo mudaria. As pessoas na África Centro-Oeste começaram a experimentar a agricultura, cultivando inhame, legumes, pimentas e cabaças que se tornariam alimentos básicos da dieta da África subsaariana. Essas pessoas falavam línguas pertencentes à família das línguas bantu e, há cerca de 4.000 anos, começaram a se mover.
Primeiro, eles seguiram para o leste através da floresta tropical central. Eventualmente, os descendentes desses migrantes chegaram aos confins da África Austral. Mais tarde, outros falantes de bantu que haviam permanecido na África Ocidental também começaram a viajar pela costa ocidental. Como eles viajaram por um período de séculos, eles deslocaram e absorveram muitos outros grupos de caçadores-coletores que já viviam em toda a África. Seu conhecimento agrícola e tecnológico também se difundiu para outros grupos locais. Eles muitas vezes se casavam, às vezes adotando práticas culturais locais das pessoas que encontravam. As línguas que eles trouxeram de sua terra natal ancestral se espalharam por toda a África subsaariana, e hoje a maioria das línguas da África subsaariana são bantu.
A genética dos haplogrupos maternos
Detalhes científicos
Seu haplogrupo é determinado pelo seu DNA mitocondrial.
A cada geração, as mães passam cópias de seu DNA mitocondrial (mtDNA) para seus filhos. Enquanto a maior parte do seu genoma existe em 23 pares de cromossomos que trocam peças entre gerações em um processo chamado recombinação , o mtDNA é transmitido sem embaralhar. Devido a esse padrão incomum de herança, o mtDNA contém informações ricas sobre linhagens maternas.
Um pequeno número de alterações no DNA, chamadas mutações, geralmente ocorrem de uma geração para a seguinte. Como o mtDNA não se recombina entre gerações, essas mutações se acumulam em padrões que marcam exclusivamente linhagens individuais. Os cientistas podem comparar as diferenças de sequência resultantes da construção de uma árvore. Esta árvore mostra como as linhagens maternas se relacionam umas com as outras, incluindo a observação de que todas elas compartilham um ancestral comum mais recente de aproximadamente 150.000 a 200.000 anos atrás.
O termo "haplogrupo" refere-se a uma família de linhagens que compartilham um ancestral comum e, portanto, um conjunto particular de mutações. Identificamos seu haplogrupo determinando quais ramos da árvore do mtDNA correspondem ao seu DNA. Como as linhagens mais próximas tendem a compartilhar raízes geográficas, seu haplogrupo pode fornecer informações sobre as origens de alguns de seus ancestrais de linha materna.
Os haplogrupos maternos são nomeados com sequências de letras e números que refletem a estrutura da árvore e como os ramos se relacionam entre si.
Referências
- Abu-Amero KK et al. (2007). "Influências do DNA mitocondrial eurasiano e africano na população da Arábia Saudita." BMC Evol Biol. 7:32.
- Barbieri C et al. (2014). "Migração e interação em uma zona de contato: variação do mtDNA entre falantes de bantu na África Austral." PLoS Um. 9(6):e99117.
- Behar DM et al. (2012). "Uma reavaliação "copernicana" da árvore do DNA mitocondrial humano desde sua raiz." Am J Hum Genet. 90(4):675-84.
- Beleza S et al. (2005). "O legado genético das migrações bantu ocidentais." Hum Genet. 117(4):366-75.
- Bodner M et ai. (2012). "A rápida disseminação costeira dos primeiros americanos: novos insights dos genomas mitocondriais do Cone Sul da América do Sul." Genoma Res. 22(5):811-20.
- Brandstätter A et al. (2004). "Sequências de região de controle de DNA mitocondrial de Nairobi (Quênia): inferindo parâmetros filogenéticos para o estabelecimento de um banco de dados forense." Int J Legal Med. 118(5):294-306.
- Cerný V et al. (2004). "Sequências de mtDNA de populações de língua chadica do norte de Camarões sugerem suas afinidades com o leste da África." Ann Hum Biol. 31(5):554-69.
- Cerný V et al. (2006). "MtDNA de nômades Fulani e suas relações genéticas com populações sedentárias vizinhas." Hum Biol. 78(1):9-27.
- Cerný V et al. (2007). "Um corredor bidirecional no cinturão do Sahel-Sudão e as características distintivas das populações da Bacia do Chade: uma história revelada pelo genoma do DNA mitocondrial." Ann Hum Genet. 71 (Pt 4): 433-52.
- Chan EK et ai. (2015). "Linha do tempo revisada e distribuição das primeiras linhagens maternas humanas divergentes na África Austral." PLoS Um. 10(3):e0121223.
- Coia V et al. (2005). "Comunicação breve: variação do mtDNA no norte de Camarões: falta de linhagens asiáticas e implicações para a migração de volta da Ásia para a África subsaariana." Am J Phys Anthropol. 128(3):678-81.
- Destro-Bisol G et ai. (2004). "A análise da variação da região hipervariável 1 do mtDNA sugere que os pigmeus orientais e ocidentais divergiram antes da expansão Bantu." Sou Nat. 163(2):212-26.
- Ely B et ai. (2006). "DNAs mitocondriais afro-americanos geralmente correspondem a mtDNAs encontrados em vários grupos étnicos africanos". BMC Biol. 4:34.
- Fadhlaoui-Zid K et al. (2004). "Heterogeneidade do DNA mitocondrial em berberes da Tunísia." Ann Hum Genet. 68 (Pt 3): 222-33.
- Fernandes V et ai. (2012). "O berço árabe: relíquias mitocondriais dos primeiros passos ao longo da rota sul para fora da África." Am J Hum Genet. 90(2):347-55.
- Fu Q et ai. (2016). "A história genética da Idade do Gelo na Europa." Natureza. 534(7606):200-5.
- González AM et al. (2003). "Afinidades de DNA mitocondrial na orla atlântica da Europa." Am J Phys Anthropol. 120(4):391-404.
- Jackson BA et ai. (2005). "Diversidade genética do DNA mitocondrial entre quatro grupos étnicos em Serra Leoa." Am J Phys Anthropol. 128(1):156-63.
- Kayser M. (2010). "A história genética humana da Oceania: visões próximas e remotas da dispersão." Curr Biol. 20(4):R194-201.
- Kivisild T et ai. (2004). "Herança do DNA mitocondrial etíope: rastreando o fluxo de genes através e ao redor do portão das lágrimas." Am J Hum Genet. 75(5):752-70.
- López S et al. (2015). "Dispersão humana fora da África: um debate duradouro". Evol Bioinform Online. 11 (Suplemento 2): 57-68.
- Lhamas B et ai. (2016). "Antigo DNA mitocondrial fornece escala de tempo de alta resolução do povoamento das Américas." Sci Adv. 2(4):e1501385.
- Majumder PP. (2010). "A história genética humana do sul da Ásia." Curr Biol. 20(4):R184-7.
- Malaspinas AS et al. (2016). "Uma história genômica da Austrália aborígene." Natureza. 538(7624):207-214.
- Mellars P et ai. (2013). "Perspectivas genéticas e arqueológicas sobre a colonização humana moderna inicial do sul da Ásia." Proc Natl Acad Sci US A. 110(26):10699-704.
- Metspalu M et ai. (2004). “A maioria dos limites de mtDNA existentes no sul e sudoeste da Ásia provavelmente foram moldados durante o assentamento inicial da Eurásia por humanos anatomicamente modernos”. BMC Genet. 5:26.
- Praça S et ai. (2003). "Unindo os pilares de Hercules: sequências de mtDNA mostram fluxo gênico multidirecional no Mediterrâneo ocidental." Ann Hum Genet. 67 (Pt 4): 312-28.
- Quintana-Murci L et al. (2004). "Onde o oeste encontra o leste: a complexa paisagem do mtDNA do sudoeste e do corredor da Ásia Central." Am J Hum Genet. 74(5):827-45.
- Rando JC et ai. (1998). "A análise de DNA mitocondrial de populações do noroeste da África revela trocas genéticas com populações europeias, do Oriente Próximo e subsaarianas." Ann Hum Genet. 62 (Pt 6): 531-50.
- Richards M et ai. (2000). "Traçando linhagens de fundadores europeus no pool de mtDNA do Oriente Próximo." Am J Hum Genet. 67(5):1251-76.
- Rito T et ai. (2013). "As primeiras dispersões humanas modernas pela África." PLoS Um. 8(11):e80031.
- Rosa A et ai. (2004). "Perfil MtDNA dos guineenses da África Ocidental: para uma melhor compreensão da região da Senegâmbia." Ann Hum Genet. 68 (Pt 4): 340-52.
- Soares P e col. (2009). "Correção para seleção purificadora: um relógio molecular mitocondrial humano melhorado." Am J Hum Genet. 84(6):740-59.
- Stoneking M et ai. (2010). "A história genética humana do leste da Ásia: tecendo uma tapeçaria complexa." Curr Biol. 20(4):R188-93.
- Tishkoff SA et al. (2007). "A história das populações de fala de cliques da África inferida a partir do mtDNA e da variação genética do cromossomo Y." Mol Biol Evol. 24(10):2180-95.
Registro de alterações
O seu relatório pode ocasionalmente ser atualizado com base em novas informações. Este Log de Mudanças descreve as atualizações e revisões deste relatório.
| Encontro | Mudar |
|---|---|
| 8 de maio de 2017 | O relatório independente Maternal Haplogroup foi criado, apresentando novos elementos de design e conteúdo. |
| 21 de outubro de 2015 | Relatório de haplogrupos criado. |







Comentários
Postar um comentário